 产品简介
产品简介
GRO-seq(Global Run-On sequencing)核心是通过体外转录延伸标记,富集新生 RNA 并测序,直接捕获 RNA 聚合酶 II转录活性,精准绘制全基因组转录动态图谱,可区分稳态 RNA 无法反映的转录起始、暂停、延伸与终止等核心调控事件。
 实验流程
实验流程
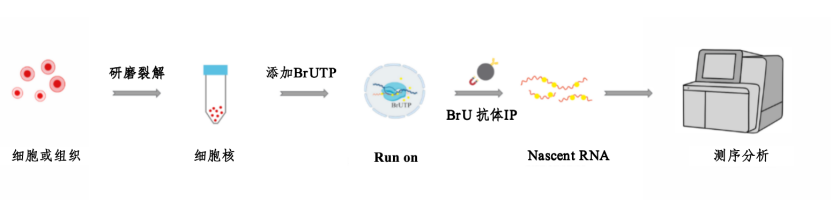
 分析内容
分析内容
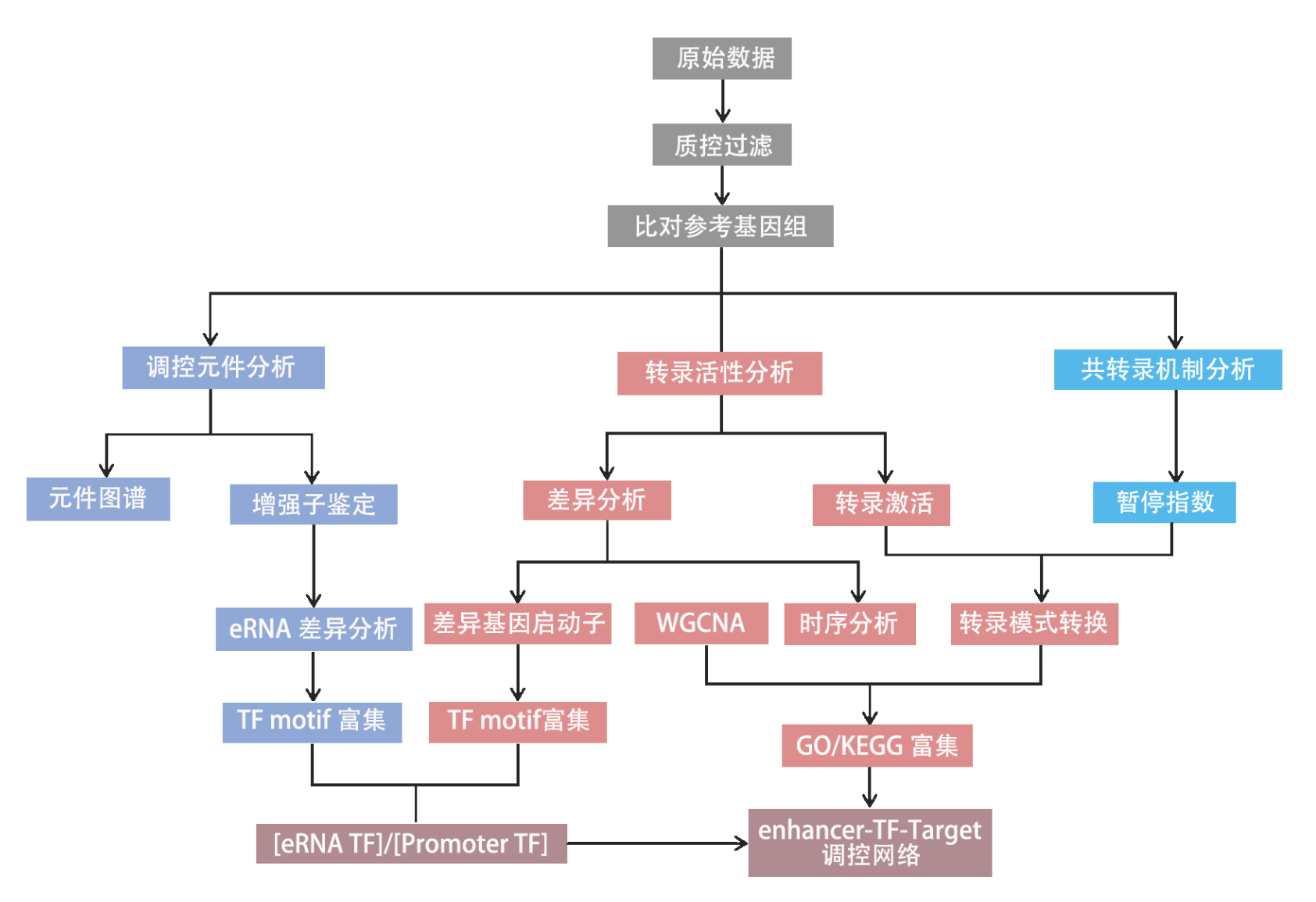
 深碳优势
深碳优势
a. 实验流程自主研发,特殊提核方式有效捕获新生RNA。
b. 不限物种及组织类型,非模式物种执行经验丰富。
c. 分析体系完善,提供全面的分析内容与多组学联合应用,一站式服务辅助文章产出。
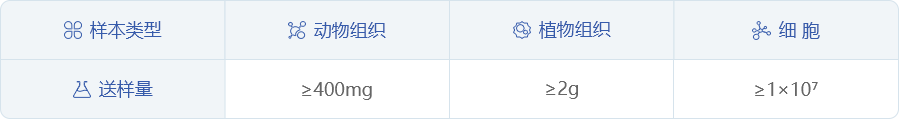
 送样建议
送样建议
a. 组织或细胞液氮速冻后干冰寄送。
b. 不同类型样本推荐送样量如下:
 已发表文献
已发表文献
1.Zhu J, Liu M, Liu X, et al. RNA polymerase II activity revealed by GRO-seq and pNET-seq in Arabidopsis[J]. Nature Plants, 2018, 4(12): 1112-1123.
2.Xie Y, Chen Y, Li Z, et al. Enhancer transcription detected in the nascent transcriptomic landscape of bread wheat[J]. Genome Biology, 2022, 23(1): 109.
3.Liu M, Zhu J, Huang H, et al. Comparative analysis of nascent RNA sequencing methods and their applications in studies of cotranscriptional splicing dynamics[J]. The Plant Cell, 2023, 35(12): 4304-4324.
4.Flynn N. Narrowing numerous nascent RNA-sequencing strategies[J]. The Plant Cell, 2023, 35(12): 4197-4198.
5.Zhu M, Liu M, Dong Z. Monitoring transcription by nascent RNA sequencing in crop plants[J]. New Crops, 2025, 2: 100031.
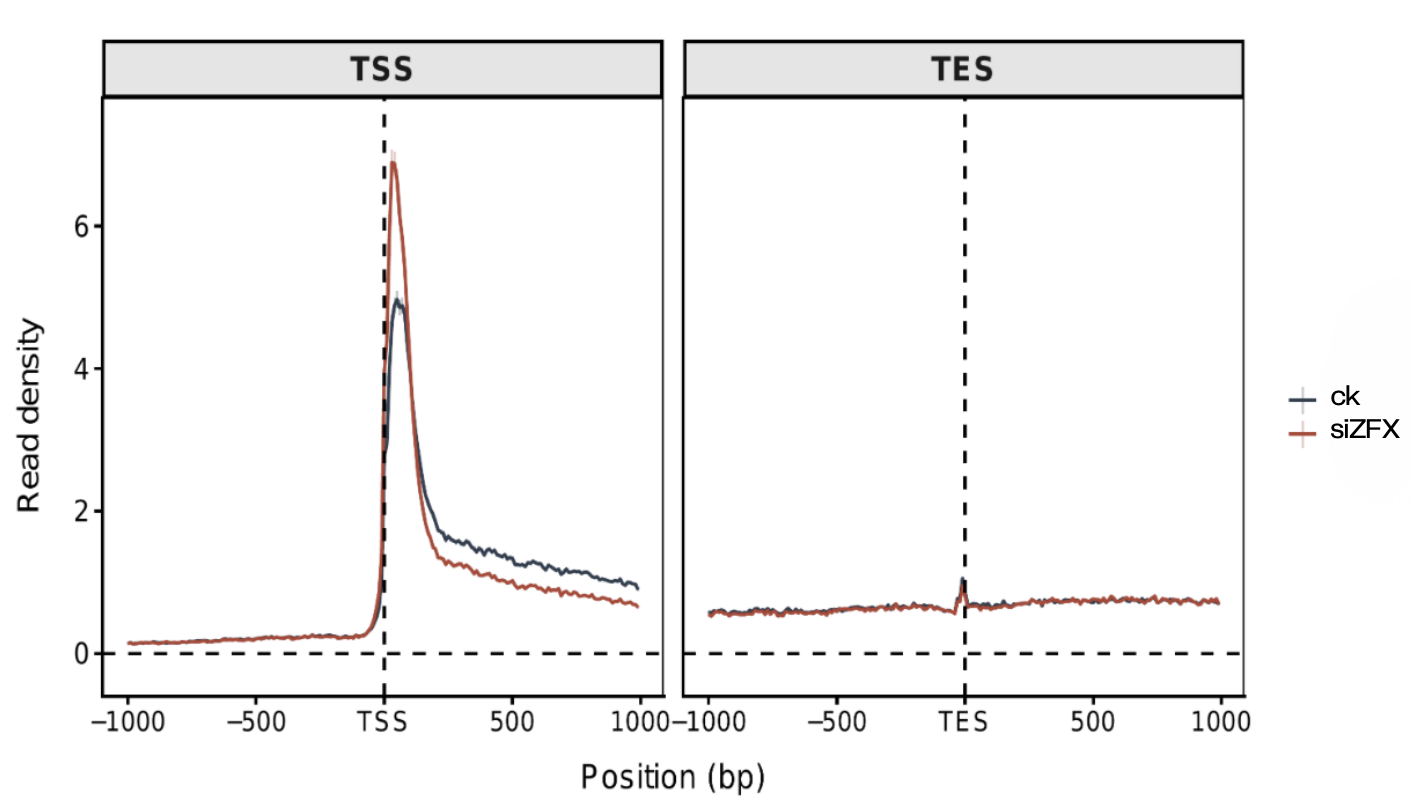
转录图谱分析
通过在基因组范围内绘制转录起始位点(TSS)和转录终止位点(TES)附近的信号强度分布图,评估基因在不同处理组中的转录动态变化情况。反映了基因转录RNA的状态,包括起始、暂停、延伸、终止等过程。
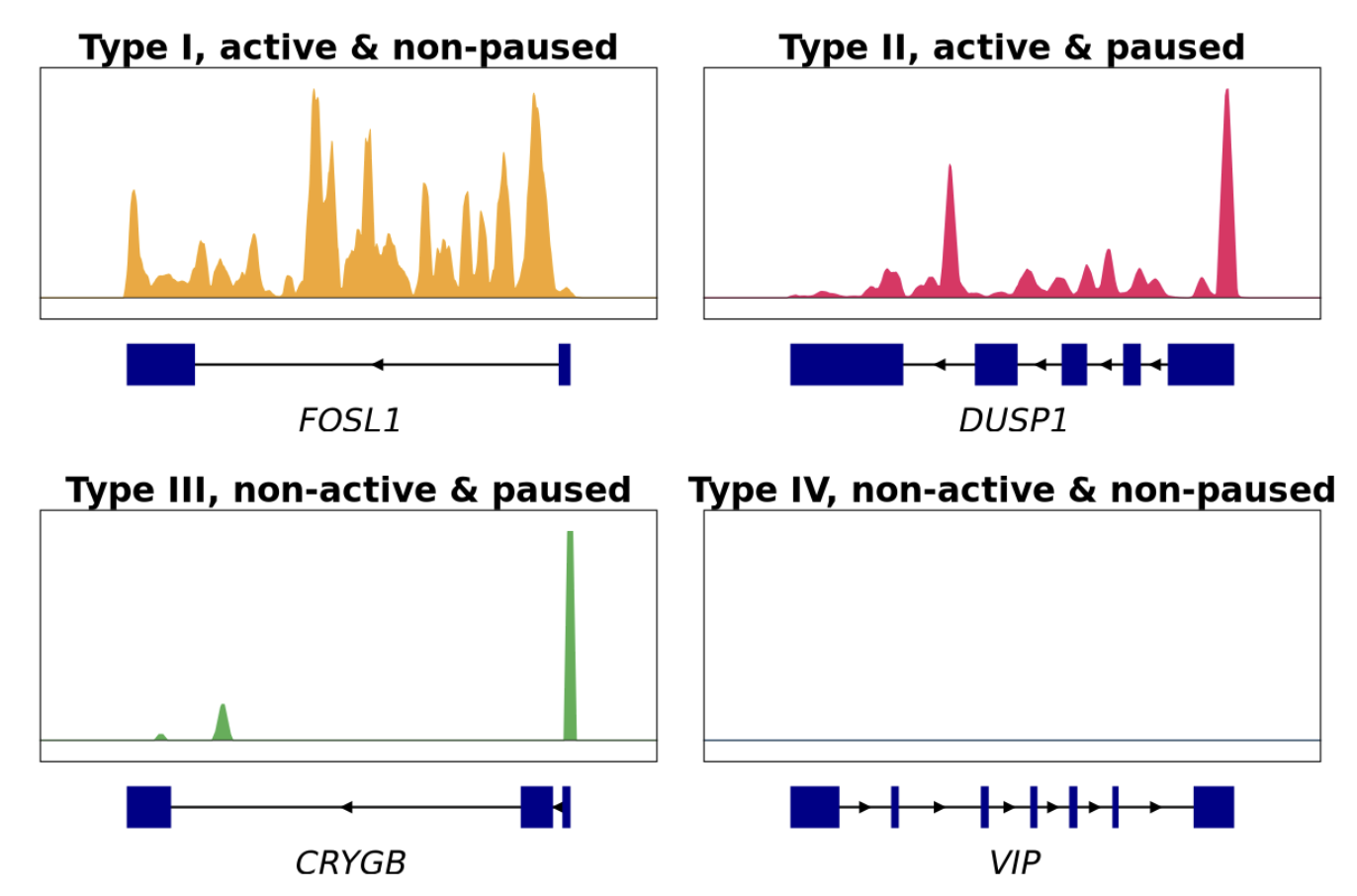
转录状态分析
依据转录活性和暂停指数(PI)对基因的转录状态进行分类及功能富集分析。
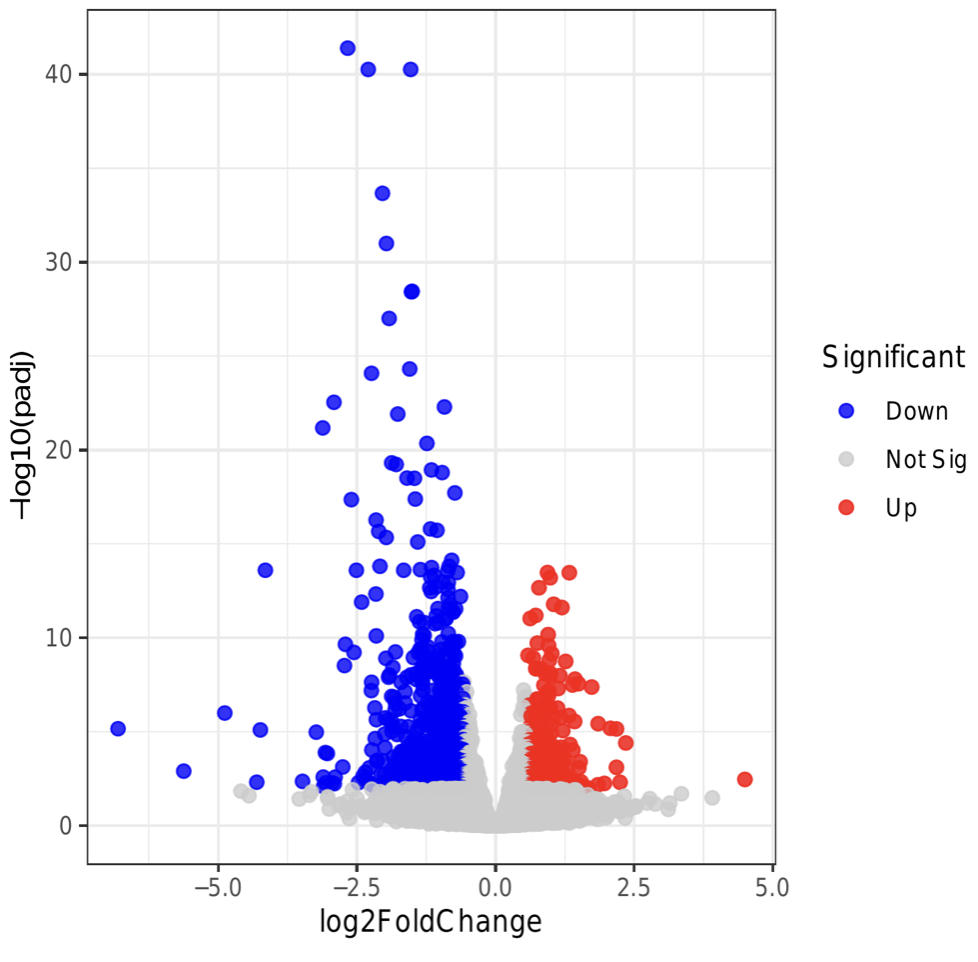
增强子鉴定及差异分析
对增强子进行鉴定,确定其在不同样本中的表达活性,并通过图表展现。
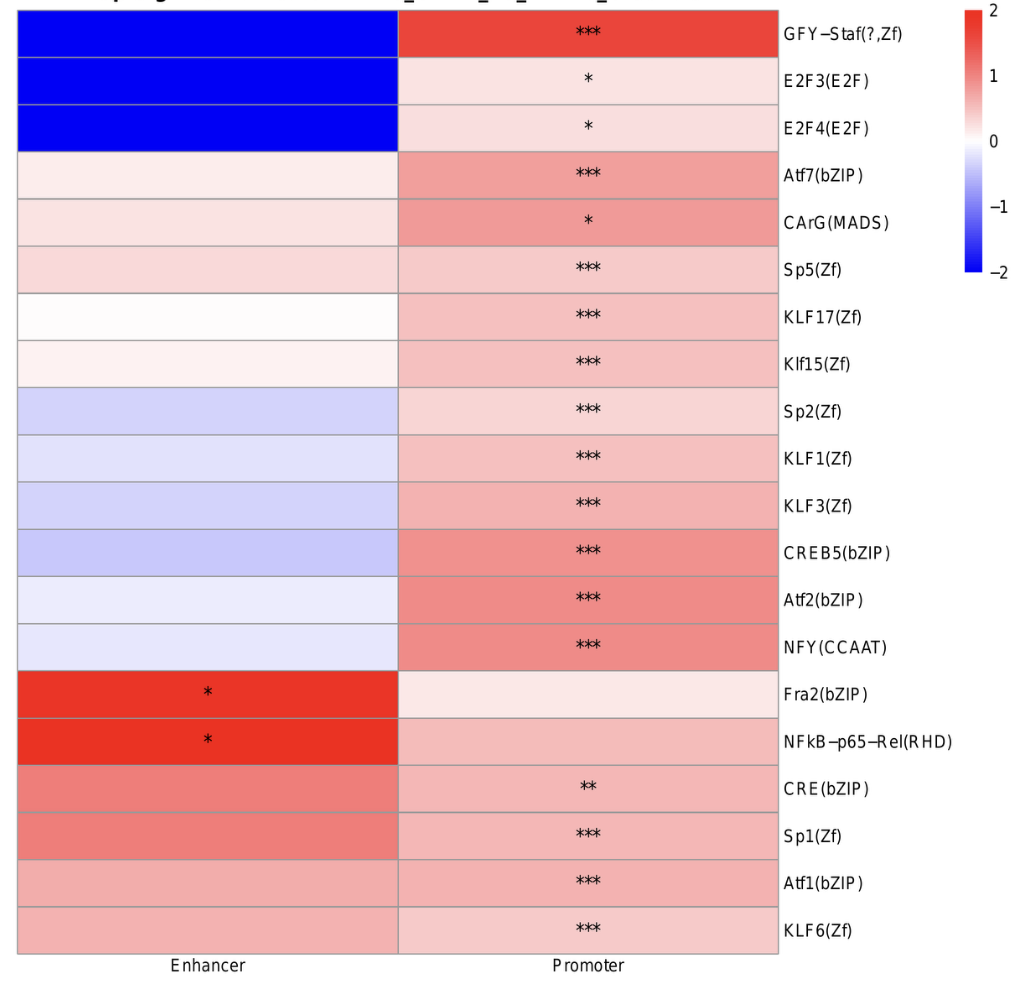
差异基因启动子区域-差异增强子区域的联合Motif分析
根据差异基因启动子区域和差异增强子区域的Motif分析结果,筛选显著富集的转录因子并集,并使用热图进行富集程度的可视化。
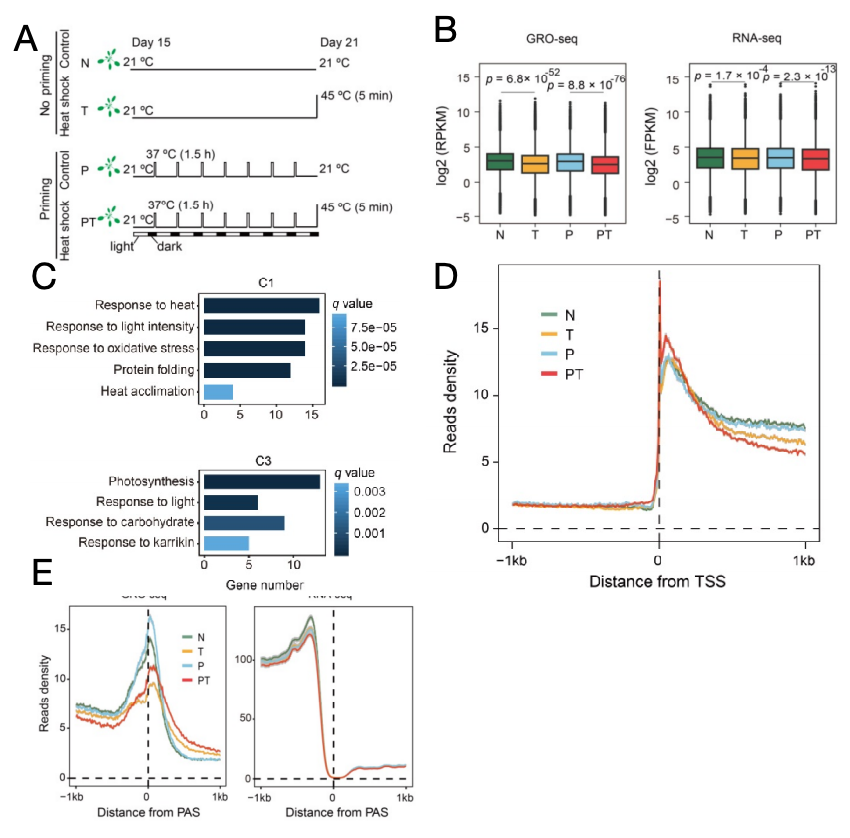
GRO-seq研究拟南芥叶对热休克的即时转录反应
期刊:J Integr Plant Biol
研究目的:研究植物形成热应激记忆早期发生的全基因组转录变化。
实验设计:对两周龄的拟南芥叶片培养一周,在采样前置于45℃环境热休克处理5min;或者在培养时每天在光暗变化结束前的1.5h置于37℃适应性培养,采样前再进行热休克处理。最后将样本用GRO-seq和RNA-seq分别进行检测,比较。
主要结果:
1.转录起始的变化:拟南芥叶热休克后通过GRO-seq检测新生RNA发现整体RNA转录水平显著下降,而RNA-seq检测显示无此明显变化;在上下调的基因当中上调集中于热、蛋白折叠、转录因子等通路,下调集中于昼夜节律、细胞分裂等非应对紧急状态的通路;通过GRO-seq检测新生RNA的密度峰,发现在近端启动子区域有38.4%的活性基因的Pol Ⅱ酶密度增加,表示转录起始位点TSS下游的转录暂停是应激状态下调控转录的主要手段。
2.转录终止的变化:通过GRO-seq检测,发现相较于对照组,在热休克的细胞中多聚腺苷酸化位点PAS下游500 bp左右出现较高信号,表明短时间的热休克显著降低聚腺苷酸化和终止效率,然而RNA-seq检测未能发现这种变化。
GRO-seq通过检测eRNA确定与哮喘相关的非编码区功能性遗传变异
期刊:Nature Communications
研究目的:根据eRNA转录特征筛选哮喘非编码区SNP,鉴定与哮喘相关的功能性遗传变异,并研究其分子机制。
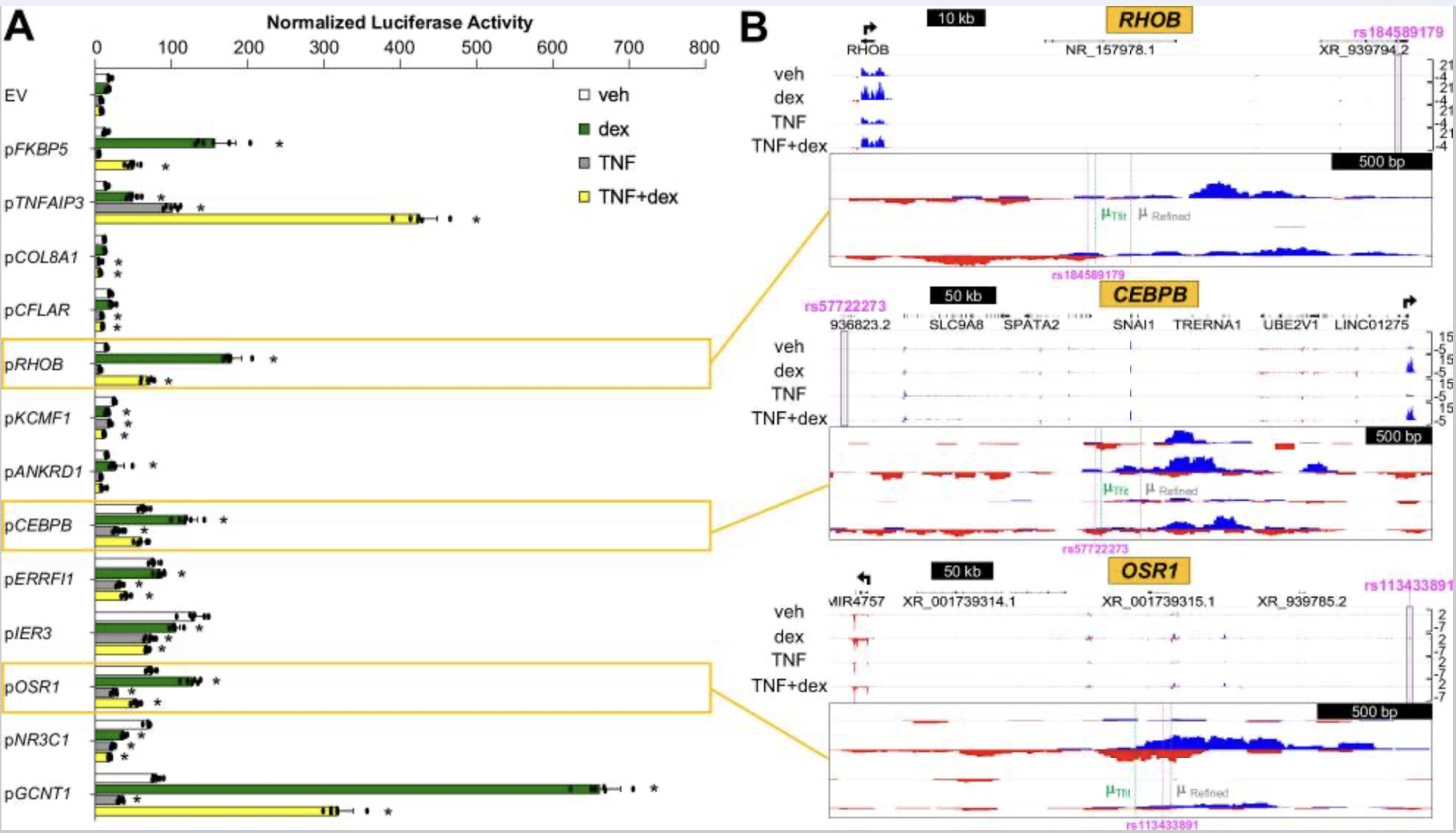
实验设计:构建哮喘细胞模型(对照组veh、地塞米松处理组dex、TNF炎症处理组TNF、共同处理组TNF+dex),使用GRO-seq分析差异eRNA;联合GERA队列GWAS数据鉴定μ-SNP(增强子区域SNP),并通过荧光素酶报告系统、基因编辑、染色质构象分析进行验证。
主要结果:
1.μ-SNP筛选:GRO-seq鉴定出1714个差异表达eRNA,与GERA队列联合分析筛选出22个高置信μ-SNP。
2.荧光素酶报告系统验证:78%(7/9)高置信μ-SNP区域表现出显著活性动态变化(图A),说明高置信μ-SNP区域可能具有生物学调节功能。
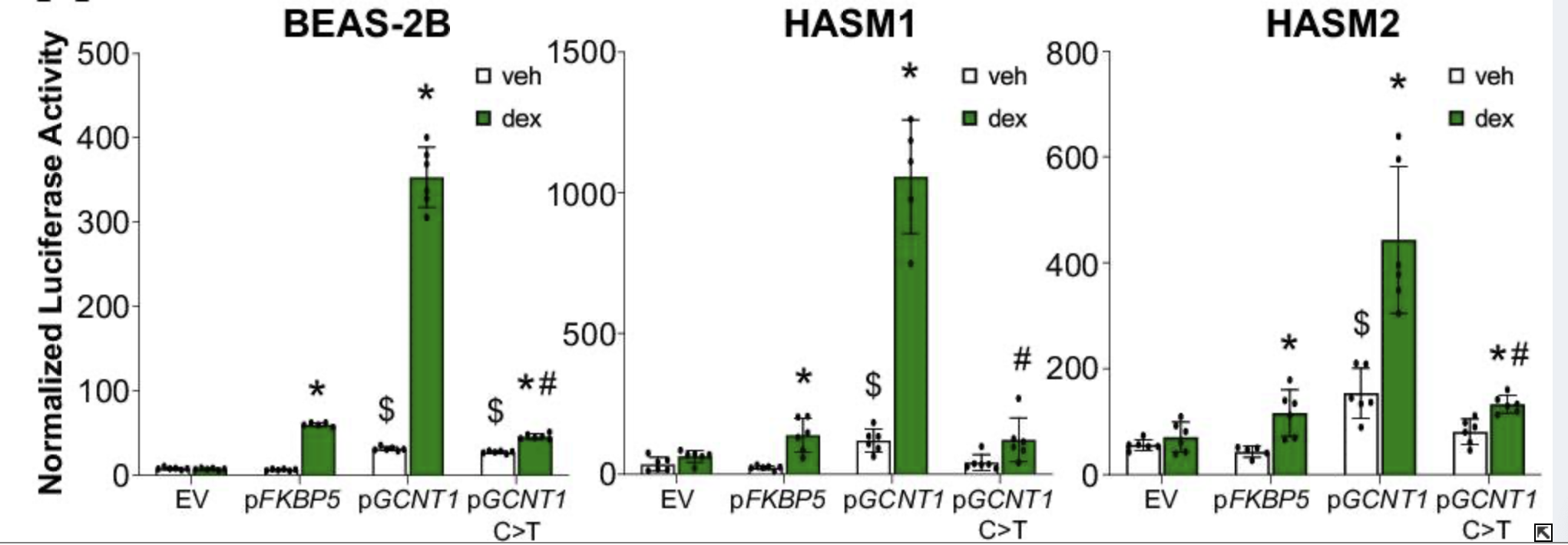
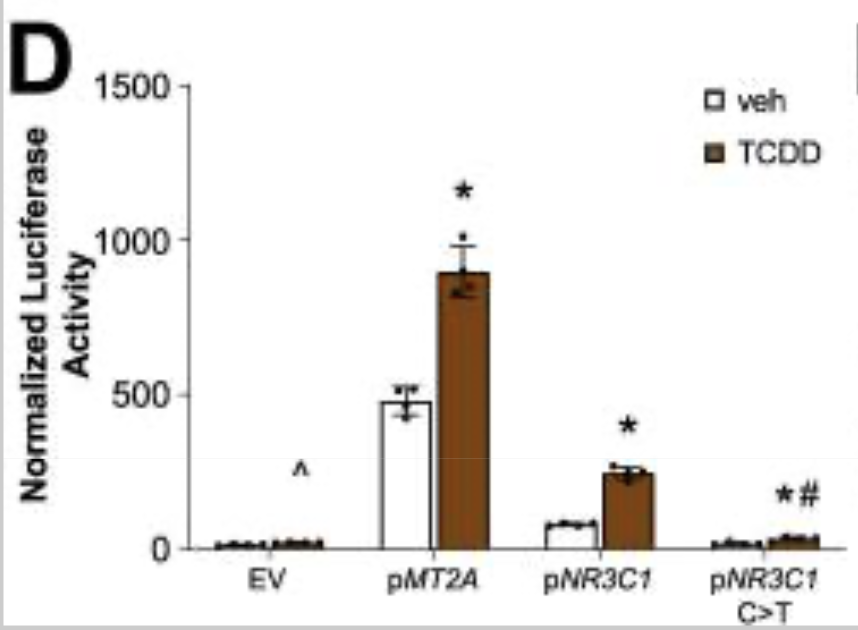
3.关键μ-SNP验证:在22个高置信μ-SNP中筛选出2个进行验证;rs149411423 变异破坏调节 GCNT1 表达的功能性糖皮质激素反应元件,降低dex诱导的GCNT1表达(图B);rs258760变异破坏调节 NR3C1 表达的反应元件,影响空气污染物(如木烟颗粒TCDD)诱导的NR3C1表达(图C)。
参考文献:
1.Liu M, Zhu J F, Dong Z C. Immediate transcriptional responses of Arabidopsis leaves to heat shock[J]. Journal of Integrative Plant Biology,2020,62(00):1-20.
2.Sasse S K,Dahlin A,Sanford L,et al. Enhancer RNA transcription pinpoints functional genetic variants linked to asthma[J]. Nature Communications,2025,16:2750.


